【每天一个知识点】轨迹分析(Trajectory inference or Pseudotime analysis)
单细胞RNA测序中的轨迹分析是揭示细胞动态演化路径的关键方法,通过基因表达变化推断伪时间顺序,构建细胞状态转变轨迹。该方法广泛应用于发育、疾病进展和治疗应答等研究。主流工具包括Monocle3、Slingshot、PAGA等,支持不同分析需求。核心流程包含数据预处理、聚类、轨迹构建和可视化等步骤,通过伪时间和基因表达趋势图展示细胞演化路径。典型可视化采用UMAP背景图,标注起点、路径、分支和伪时间
·
单细胞RNA测序(scRNA-seq)中的轨迹分析(Trajectory inference or Pseudotime analysis)是用来揭示细胞在动态生物过程中的演化路径(如分化、发育、疾病进展)的关键分析方法。它尝试在没有真实时间点的情况下,根据基因表达的变化趋势推断“伪时间”顺序,从而构建细胞状态的连续转变轨迹。
📌 一、轨迹分析的应用场景
| 应用 | 举例 |
|---|---|
| 细胞发育过程重建 | 干细胞 → 前体细胞 → 成熟细胞 |
| 癌症进展分析 | 正常 → 癌变 → 转移状态 |
| 治疗应答轨迹 | 初始 → 药物响应 → 耐药细胞 |
| 免疫应答过程 | T细胞活化与疲劳状态识别 |
🧰 二、常见轨迹分析工具
| 工具 | 特点 | 编程语言 |
|---|---|---|
| Monocle3 | 主流方法,支持graph-based轨迹 | R |
| Slingshot | 兼容多种降维与聚类工具 | R |
| PAGA (Scanpy) | 适合大规模数据,图结构稳定 | Python |
| Palantir | 用于命运概率分析、结合diffusion map | Python |
| DPT (Diffusion Pseudotime) | 基于扩散图计算伪时间 | Python |
| scVelo | 融合RNA velocity,推测方向性 | Python |
🧭 三、轨迹分析核心流程(通用)
-
数据预处理:标准化 → 降维(如PCA、UMAP)
-
聚类:初步细胞状态分群
-
构建轨迹图:基于邻接关系(graph-based)、扩散映射或最短路径
-
定义起始状态(root cell)或发育起点
-
计算伪时间(pseudotime):按轨迹推断每个细胞的位置
-
可视化与分析:
-
Pseudotime vs. gene expression(趋势图)
-
不同分支的命运路径
-
Marker基因的表达动态
-
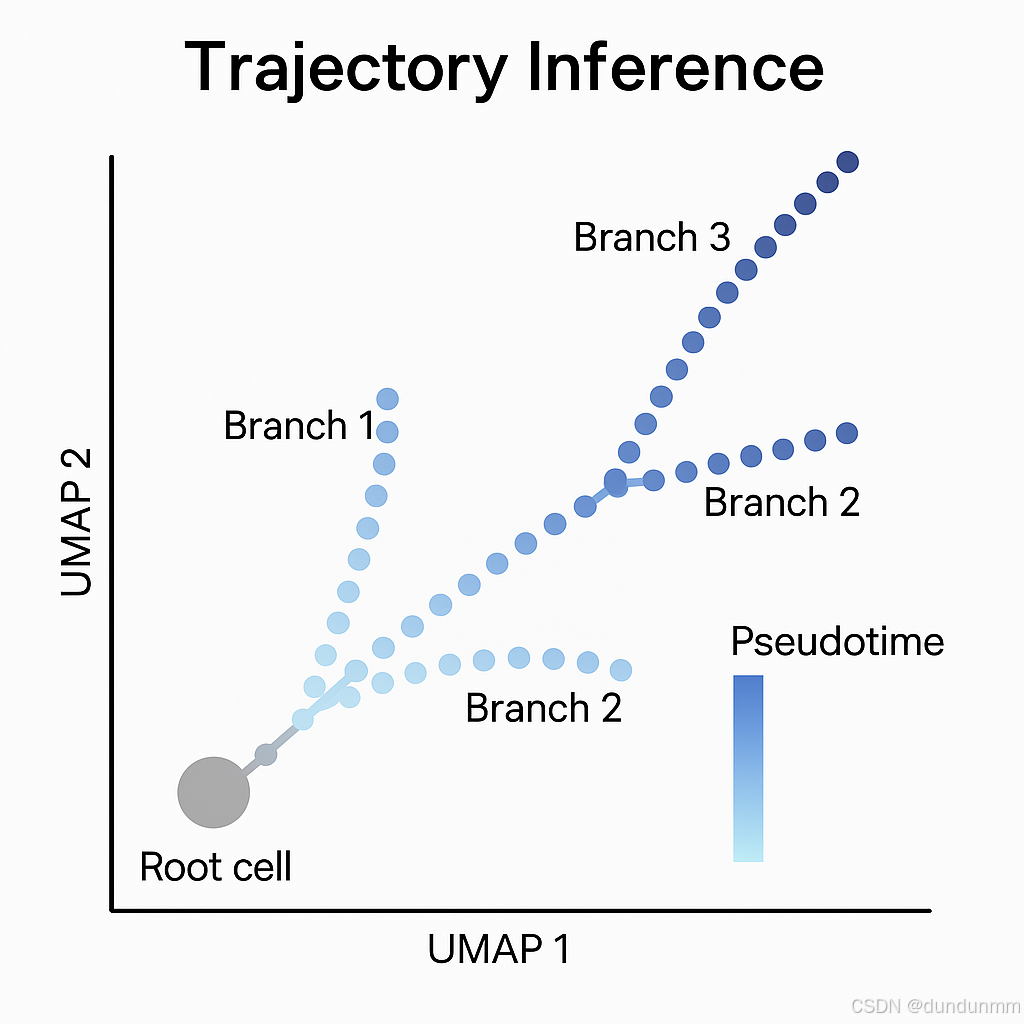
📊 四、Palantir轨迹分析示意图(含伪时间)
如果你需要图示,这是一张典型的轨迹分析可视化图结构,可用UMAP背景图 + 轨迹路径 + 分支标注:
-
起点:灰色圆点表示root cell
-
路径:细胞状态演化方向用线连接
-
分支:用不同颜色标识不同命运路径
-
Pseudotime:通过颜色梯度表示(例如浅蓝→深蓝)
更多推荐
 已为社区贡献3条内容
已为社区贡献3条内容






所有评论(0)